
lncRNA测序
 技术优势
技术优势
 技术路线
技术路线
 分析内容
分析内容
| 原始数据产出统计与预处理 | 原始数据产出统计与预处理 | mRNA数据分析 |
|---|---|---|
| 与参考基因组比对及统计; | lncRNA重新注释,获取lncRNA在染色体上附近的基因,以及位于基因功能区域; | |
| 基因表达丰度分析; | lncRNA差异表达分析; | |
| GO功能分类; | 采用cis和trans两种方式预测lncRNA调控的靶基因; | |
| KEGG代谢通路分析; | 对差异表达lncRNA的靶基因进行GO和pathway富集性分析; | |
| 基因差异表达谱分析; | lncRNA与mRNA共表达分析,构建lncRNA与mRNA相互作用网络。 | |
| 差异表达基因的GO功能富集性分析,KEGG代谢通路富集性分析; |
 样本类型
样本类型
 案例展示
案例展示
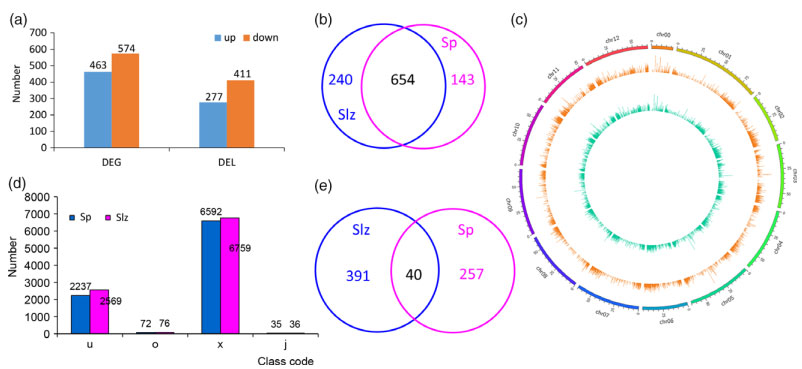
 参考文献
参考文献
 结果展示
结果展示
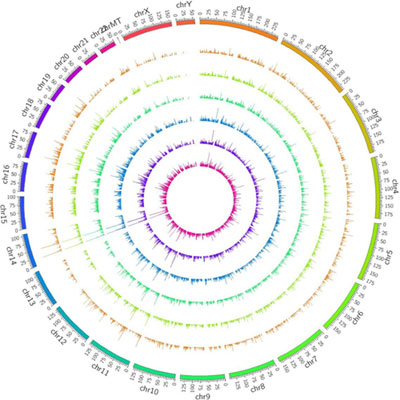
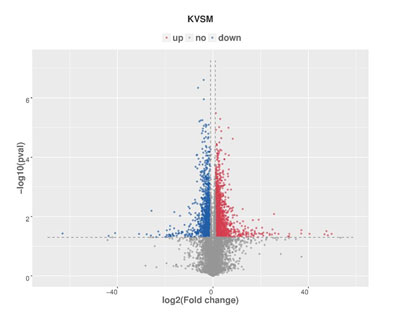
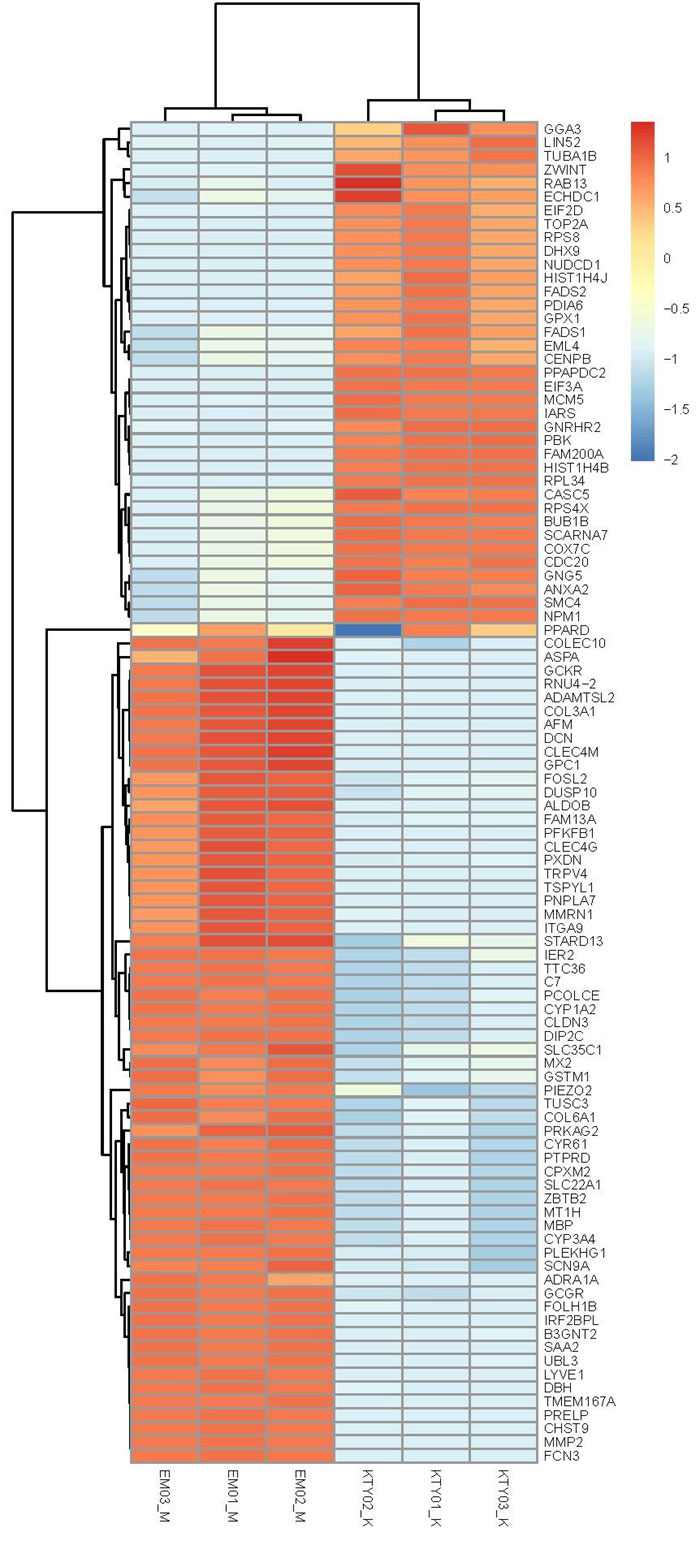
 常见问题
常见问题

扫一扫,反馈当前页面
和元生物